단일 분자 생물물리학, 생명체 이해 돕는 또 다른 접근법
DNA에 작용하는 다른 효소들의 운동메커니즘 연구에 기여
점차 전체 속의 개개인이 중요해지는 요즘 사회의 흐름 속에서 과학적 접근 방식에도 변화가 일고 있다. 특히 물리학 분야에서 필자가 연구하고 있는 ‘단일 분자 생물물리학(Single-molecule Biophysics)’이 그 대표적인 예이다. 생명현상을 연구하는데 있어서 세포 및 생체물질들의 집단 평균(ensemble average, 어떤 시스템에서 가능한 모든 상태의 통계적 평균)이 주는 정보 속에 숨겨져 있는 개개 분자들이 일으키는 현상을 관찰하고자 하는 것이 이 분야의 목적이다. 즉, 앞의 영화관에서 ‘G15번 자리에 앉아 있는 뿔테안경을 낀 남자가 공포영화의 한 장면을 보고 소리를 지르며 눈을 감았다.’라고 좀 더 구체적으로 기술하고자 하는 것이다. 실제로 생명현상에 대한 이러한 접근 방식은 많은 성과를 거두었다. 몇 가지 예로 세포 내에서 물질을 수송하는 운동단백질이 마치 사람이 두 다리로 짐을 지고 걸어가는 형상으로 운동한다는 것을 밝혀내는가 하면 DNA 복제에 관여하는 단백질이 얼마나 빠른 속도로 운동하며 주변 단백질과 어떻게 상호작용을 하는 지도 설명할 수 있게 되었다.
최근 포항공대 물리학과에서 ‘단일 분자 생물물리학’을 연구하고 있는 이종봉 교수 연구팀이 화학과 반창일 교수 연구팀과의 공동연구를 통해 DNA 염기쌍 오류 복구(mismatch repair)에 관련된 근본적인 질문 중 하나인 ‘DNA 효소들이 어떻게 특정 위치를 찾아내고 그 신호를 전달하는지’에 대한 해답을 찾았다. 기존의 집단 평균적 실험 결과들로는 규명하기 힘들었던 구체적인 메커니즘을 단일 분자 기술을 이용해서 밝혀낸 것이다. 연구결과는 세계 최고 권위의 과학전문지인 ‘네이처’ 자매지 ‘네이처 스트럭처럴 몰레큘러 바이올로지’ 온라인 속보에 게재되었다.
우리 몸의 각 세포들은 약 30억 개의 DNA를 가지고 있는데, DNA를 복제하거나 재조합하는 과정에서 염기쌍 오류가 발생할 수 있다. 염기쌍 오류란 DNA 상의 특정 염기가 바뀌어서 A-T, G-C의 쌍을 이루지 못하는 현상을 말한다. 이러한 오류가 누적되면 돌연변이가 생겨 세포 기능에 심각한 문제를 일으키거나 암세포가 발생하기도 한다.
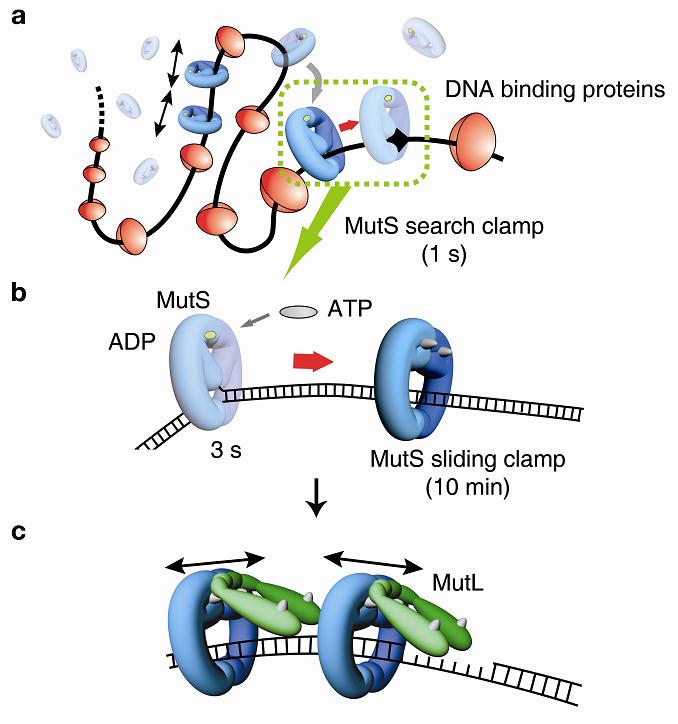
다행히 우리 몸에는 이러한 DNA 오류를 자동적으로 복구하는 시스템(DNA mismatch repair system)이 존재한다. 생명 현상의 많은 경우가 그렇듯이 여기에는 수많은 단백질들이 관여하는데 그 중 가장 먼저 DNA 오류를 인식하고 오류복구 시스템을 작동시키는 방아쇠 역할을 하는 단백질이 MutS(뮷 에스) 단백질이다. 오래 전부터 DNA 오류 복구 시스템을 연구하는 과학자들에 의해서 MutS 단백질의 존재가 알려졌고 2000년도에 들어와서는 그 구조가 밝혀졌지만 이 단백질이 어떻게 30억 개나 되는 DNA 중 1개 존재하는 오류 염기쌍을 찾아가는지, 오류 염기쌍을 인식한 이후 오류를 복구시키는 다른 단백질들에는 어떻게 신호를 전달하는지는 여전히 숙제로 남아있었다.
광학적 한계로 나노미터 크기(1 나노미터는 10억분의 1m로, 성인 머리카락 굵기의 10만분의 1에 해당된다.)의 생체 분자들의 상호 작용을 직접 관찰하기란 불가능하다. 기술의 발전으로 전자현미경을 통해 나노미터 크기의 물체를 관찰 할 수 있게 되었지만 전자현미경은 시료를 응고시켜야 하는 문제 때문에 실시간으로 생명 현상을 관찰하기에는 부적합하다. 따라서 물리학과 이종봉 교수 연구팀은 전반사 현미경을 이용해서 ‘형광 공명 에너지 전달 기술(FRET)’과 ‘단일입자추적(single-particle tracking)’ 등의 물리학적 연구·분석을 통해 우리 몸의 DNA 염기쌍 오류 복구 시스템을 단일분자 수준에서 연구할 수 있는 방법을 개발하였다.
연구결과 많은 사람들이 여러 가지 가설에 의한 모델로만 제시해왔던 MutS 단백질의 운동 메커니즘이 밝혀졌다. 우선 MutS 단백질이 염기쌍 오류의 유무에 상관없이 노출된 DNA에 무작위로 결합한 이후 DNA의 나선구조를 따라 일차원 회전 확산 운동을 하는 것이 관찰되었다. DNA에 염기쌍 오류가 있는지 없는지를 확인하며 오류 지점을 찾아가는 과정이다. 그러다가 목표지점인 오류 염기쌍을 찾게 되면 운동을 멈추고 오류 염기쌍에 결합한 채 꽤 오랜 시간동안 머물러 있는 것이 관찰되었다. 단백질이 정상적인 DNA 염기쌍 위를 운동할 때의 지속 시간과 비교 분석을 통해 MutS 단백질이 오류 염기쌍에 결합한 상태가 에너지적으로 더 안정함을 알 수 있었고, 이는 선행된 집단 평균적 실험 결과들과도 일치하는 결과였다. 이전까지 학계에 보고 된 바에 따르면 MutS가 오류 염기쌍을 인식한 이후에는 생체 에너지 전달 물질인 ATP와의 결합을 통해 다른 오류 복구 단백질들과 상호작용을 하게 되는데, 본 연구를 통해 MutS가 ATP와 결합한 이후 오류 지점에서 떨어져 나와 DNA에서 분리되지 않고 약 10분이라는 비교적 긴 시간 동안 DNA를 따라서 운동한다는 것을 밝혀내었다. 더군다나 연구자들이 궁금해 해왔던 ATP가 결합한 MutS 단백질의 운동 에너지원이 ATP 가수분해 에너지가 아닌 열적 요동(thermal fluctuation) 에너지임을 알아내었다. 오류 염기쌍을 인식한 이후 ATP가 결합한 MutS 단백질의 운동을 오류 염기쌍을 찾기 전 MutS의 운동과 비교해보면 100배 이상 안정함을 알 수 있었다. 이는 ATP의 결합이 MutS의 내부구조를 변화시켰음을 의미한다. 생물학적 기능을 바탕으로 생각해보면 MutS 단백질이 오류 염기쌍을 인식한 이후 DNA 상을 운동하며 3개 이상의 다른 단백질들을 찾아서 복합체를 이루어야 하기 때문에 ATP와 결합한 MutS 단백질의 운동이 더 안정된 것이 합리적이다.
본 연구를 통해 DNA 염기쌍 오류 복구의 시작을 담당하는 MutS 단백질을 실시간으로 관측함으로써 MutS 단백질의 오류 염기쌍 인식과 그 오류 염기쌍의 존재를 알리는 메커니즘을 규명하였으며, 이를 토대로 아직 밝혀지지 않은 DNA에 붙어서 작동하는 다른 효소들의 운동 메커니즘에 대한 이해를 높이는 데도 기여할 수 있게 되었다.
학문 간의 경계가 사라진 현대에 물리학의 범주에서 생물학을 연구할 수 있는 ‘단일 분자 생물물리학’이라는 분야는 인간이 속해있는 생명체에 대한 이해를 돕는 또 하나의 접근법이라 생각된다. 시대를 막론하고 자연을 탐구한다는 것은 매력적인 일이다. 필자는 대한민국 국민의 한 사람으로서 세계 28위의 위상을 자랑하는 포항공대에서 자연 현상에 대한 인류의 지식 축적에 기여할 수 있다는 것을 자랑스럽게 생각한다.


